PRUEBA PRÁCTICA-BIOINFORMÁTICA
BÚSQUEDA DE SECUENCIAS DE PROTEÍNAS EN BASES DE
DATOS


Las bases de datos biológicas se han convertido en un instrumento importante
para ayudar a los científicos a comprender y explicar los fenómenos biológicos, desde la
estructura biomolecular y su interacción, hasta el metabolismo completo de los
organismos y la comprensión de la evolución de las especies. Este conocimiento ayuda al
diagnóstico de patologías, al desarrollo de medicamentos, a la lucha contra las
enfermedades, al descubrimiento de las relaciones básicas entre las especies en la
historia de la vida...
El conocimiento biológico se distribuye entre múltiples bases de datos generales y
especializadas. Uno de los tipos de bases de datos biológicas más usados son las bases de
datos de secuencias. Estas son una gran colección de secuencias de ADN, proteínas y
otras, que se almacenan en computadoras. Se denomina 'secuencia’ al orden en que los
nucleótidos (en el ADN) o los aminoácidos (en los péptidos y proteínas) se encadenan. La
secuencia de aminoácidos de una proteína viene determinada por la secuencia de
nucleótidos del ADN del gen que la codifica.
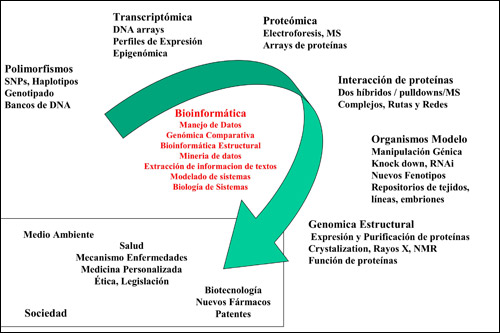
Una base de datos puede incluir secuencias de un sólo organismo, como las bases
de datos que contienen todas las proteínas de la bacteria Escherichia coli, o de la levadura
de la cerveza Saccharomyces cerevisiae o la de Homo sapiens, o puede incluir secuencias
de todos los organismos cuyo ADN ha sido secuenciado. Las bases de datos biológicas
también tienen referencias cruzadas con otras bases de datos con el número de acceso
como una forma de vincular sus conocimientos relacionados con el conjunto.
Existen bases de datos primarias, que contienen información directa de la
secuencia, estructura o patrón de expresión de ADN o proteína y, secundarias que
contienen datos e hipótesis derivados del análisis de las bases de datos primarias, como
mutaciones, relaciones evolutivas, agrupación por familias o funciones, implicación en
enfermedades, etc.
requerimiento básico para la investigación bioquímica, biomédica y biotecnológica. Para
ello, el desarrollo y uso de herramientas bioinformáticas, así como el manejo de las bases
de datos biológicas, son indispensables.
Las principales bases de datos de ADN son: EMBL-BANK en el Instituto europeo
de Bioinformática (EBI); DNA Data Bank of Japan (DDBJ) en el Centro de Información
Biológica (CIB); GenBank en el Centro Nacional de Información Biotecnológica (NCBI).
Las principales bases de datos de proteínas son: Swiss-Prot, que contiene
secuencias anotadas o comentadas, es decir, cada secuencia ha sido revisada,
documentada y enlazada a otras bases de datos; PROSITE que contiene información sobre
la estructura secundaria de proteínas, familias, dominios, etc; Protein Data Bank (PDB)
que es la base de datos de estructura terciaria 3-D de proteínas que han sido cristalizadas;
InterPro que integra la información de diversas bases de datos de estructura secundaria
como PROSITE, proporcionando enlaces a otras bases de datos e información más
extensa.
Las principales bases de datos de genomas son: Ensembl que integra genomas
eucariotas grandes como el genoma humano, ratón, rata, pez cebra, mosquito,
Drosophila melanogaster, Saccharomyces cerevisiae.
También existen motores de búsqueda como PubMedo BLAST que dan libre
acceso a diferentes tipos de bases de datos.
MATERIAL
- Ordenadores con conexión a internet
DESARROLLO DE LA PRÁCTICA
1. Accede a la base de datos Uniprot/Swiss-Prota través del enlace
http://www.uniprot.org/
2. Busca la secuencia de la proteína con código de acceso P69891. Para ello introduce
este código en la ventana “Query” y asegúrate que la búsqueda la haces en UniprotKB.
3. Explora la ficha resultado. En ella podrás encontrar el nombre de la proteína, el
organismo al que pertenece, su clasificación taxonómica, la longitud de su secuencia de
aminoácidos, su peso molecular, su función, su localización, etc. También puedes tener
acceso al análisis de su estructura primaria y a la secuencia completa de aminoácidos
entre otras informaciones.
4. Busca otras proteínas que pertenezcan a la misma familia de P69891. Para ello accede
a la familia de proteínas a la que pertenece esta proteína pulsando en el correspondiente
enlace que aparece en la ficha de resultados.
5. Las bases de datos biológicas suelen estar conectadas a motores de búsqueda que
pueden proporcionar información adicional. Con la herramienta bioinformática BLAST
podemos identificar proteínas idénticas u homólogas en otros organismos.
Pincha en BLAST y podrás identificar esta proteína en otros organismos. El resultado de la
búsqueda está ordenado por el porcentaje de identidad que hay entre la secuencia
problema que has introducido y las secuencias resultantes de la búsqueda.
Los resultados de la búsqueda pueden aparecer en varias páginas. Para moverte por estas
páginas usa ‘next’ y ‘previous’.
6. Estos motores de búsqueda también pueden proporcionar información adicional
taxonómica. Accede a la ventana ‘taxonomy’ y podrás encontrar los organismos en los
que se encuentra esta proteína agrupados por especies.
7. La consulta de otras bases de datos puede proporcionar información relevante.
A) Protein Data Bank (PDB) (http://www.rcsb.org) proporciona información
estructural 3D de las proteínas cuya estructura ha sido determinada, indicando el método
que se ha empleado para determinar la estructura y la resolución atómica a la que ha sido
resuelta en angstroms (Å). Este dato es importante para conocer la calidad de la
estructura. Las proteínas tienen una estructura primaria, secundaria, terciaria y
cuaternaria. La estructura primaria se refiere a la secuencia de aminoácidos. La estructura
secundaria es la disposición espacial local del esqueleto proteico, debido a la formación
de puentes de hidrógeno entre los átomos que forman el enlace peptídico, sin hacer
referencia a la cadena lateral. Los elementos de estructura secundaria pueden ser
ordenados como las hélices alfa y láminas beta (u hojas plegadas beta) o desordenados.
La estructura terciaria es el modo en que la cadena proteíca se pliega en el espacio. La
estructura cuaternaria deriva de la conjunción de varias cadenas peptídicas que,
asociadas, conforman un multímero, que posee propiedades distintas a la de sus
monómeros componentes.
B) GenBank (http://www.ncbi.nlm.nih.gov) contiene información de todos los
genomas secuenciados así como de su distribución cromosómica.
1.-Indica a qué proteína corresponde el código de acceso P69891 (0,5 ptos)
a) insulina de humanos (Homo sapiens)
b) hemoglobina de humanos (Homo sapiens)
c) queratina de humanos (Homo sapiens)
d) hemoglobina de ratón (Mus musculus)
e) elastina de humanos (Homo sapiens)
2.- ¿Cuántos aminoácidos y qué peso molecular tiene la proteína P69891? (0,5 ptos)
a) 250 aa y 43.000 Da
b) 115 aa y 25.200 Da
c) 1345 aa y 243.800 Da
d) 147 aa y 16.140 Da
e) 943 aa y 123.760 Da
3.- ¿A qué familia pertenece la proteína P69891? (0,5 ptos)
a) amilasas
b) globinas
c) flavinas
d) ATPasas
e) citocromos
4.-Indica qué proteína de la siguiente lista pertenece a esta familia (0,5 ptos)
a) ferredoxina
b) mioglobina
c) actina
d) plastocianina
e) citocromo c
5.-Con el motor de búsqueda BLAST busca proteínas idénticas u homólogas a P69891
en otros organismos. Indica cuál de las siguientes proteínas tiene una identidad
inferior al 80%. Ten en cuenta que los resultados pueden estar listados en varias
páginas. (0,5 ptos)
a) hemoglobina subunidad gamma-2 de mono capuchino (Cebus apella)
b) hemoglobina subunidad gamma-1 de gorila (Gorilla gorilla)
c) hemoglobina subunidadbeta-H1de ratón (Mus musculus)
d) hemoglobina subunidad gamma de elefante de la india (Elephas maximus)
e) hemoglobina subunidad épsilon-1 de cabra (Capra hircus)
6. El resultado de BLAST también proporciona información taxonómica. ¿Cuántas
especies de primates con genomas conocidos tienen una proteína idéntica u homóloga
a P69891? En la pestaña ‘taxonomy’ y moviéndote a través de ella podrás encontrar
esta información. (0,5 ptos)
a) menos de 120 especies
b) al menos 137 especies
c) menos de 40 especies
d) ninguna
e) más de 500 especies
7. Accede a Protein Data Bank (PDB) y responde a la pregunta ¿Se conoce la estructura
3D de la proteína P69891? Si es conocida su estructura marca el método que se ha
usado para su determinación y la resolución atómica. (1,5 ptos)
a) no se conoce
b) Difracción de rayos X a 1.25Å
c) Resonancia magnética nuclear (NMR) a1.86Å
d) Resonancia magnética nuclear (NMR) a 2.52Å
e) Difracción de rayos X a 1.70Å
8.-Accede a GenBank y busca la secuencia de nucleótidos del gen que codifica para la
proteína P69891 ¿Cuáles son los primeros 20 nucleótidos de la secuencia de este gen?
(2 ptos)
a) agagtatccagtgaggccag
b) gtgaactgcactgtgacaag
c) gctataaaaaaaattagcag
d) tgtgtgtgtcagcgtgtgtt
e) taatgggaaggcaaaatctc
9.-Indica el nombre del gen que codifica para la proteína P69891 y el cromosoma
donde se localiza. (1,5 ptos)
a) HBG1, cromosoma 2
b) HBG1, cromosoma 11
c) HBE1, cromosoma 10
d) HBG2, cromosoma 11
e) HBG2, cromosoma X
10. ¿Existen hemoglobinas en plantas? Si es afirmativa la respuesta indica si se ha
determinado alguna de estas estructuras 3D proteicas y en qué especies. (2 ptos)
a) No se conocen
b) Sí, pero no se ha determinado su estructura 3D
c) Sí, en maíz (Zea mays) solamente, mediante la técnica de difracción de rayos X
d) Sí, en arroz (Oryza sativa) mediante resonancia magnética nuclear (NMR)
e) Sí, en arroz (Oryza sativa) mediante la técnica de difracción de rayos X
Fuente: IX OLIMPIADA ESPAÑOLA DE BIOLOGIA 2014. - UNIVERSIDAD DE ZARAGOZA.




No hay comentarios:
Publicar un comentario